最近は,主成分分析も機械学習の視点から使用されることが多いようだが,かなり違和感を感じる。
それはさておき,主成分分析の例示であるが,そのままでは Version 1.5.3 では動かないので,少し修正して掲載。
https://multivariatestatsjl.readthedocs.io/en/stable/pca.html
julia> using MultivariateStats, RDatasets, Plots
julia> plotly() # using plotly for 3D-interacive graphing
julia> iris = dataset("datasets", "iris"); # load iris dataset
julia> # split half to training set
# 分析に使うデータ行列は列が観察値(つまり普通のデータ行列の転置!)
Xtr = transpose(Array{Float64,2}(iris[1:2:end,1:4]));
julia> Xtr_labels = Array{String,1}(iris[1:2:end,5]);
julia> # split other half to testing set
Xte = transpose(Array{Float64,2}(iris[2:2:end,1:4]));
julia> Xte_labels = Array{String,1}(iris[2:2:end,5]);
julia> # suppose Xtr and Xte are training and testing data matrix,
# with each observation in a column
# train a PCA model, allowing up to 3 dimensions
M = fit(PCA, Xtr; maxoutdim=3)
PCA(indim = 4, outdim = 3, principalratio = 0.9957325846529409)
julia> # apply PCA model to testing set
Yte = MultivariateStats.transform(M, Xte)
3×75 Array{Float64,2}:
2.72714 2.75491 2.32396 2.65105 2.68917 …
-0.230916 -0.406149 0.646374 0.0828144 -0.17411
0.253119 0.0271266 -0.230469 0.0252853 0.231507
julia> # reconstruct testing observations (approximately)
Xr = reconstruct(M, Yte)
4×75 Array{Float64,2}:
4.86449 4.61087 5.40782 5.00775 4.90864 4.83689 …
3.04262 3.08695 3.89061 3.39069 3.08963 3.35572
1.46099 1.48132 1.68656 1.48668 1.48516 1.53664
0.10362 0.229519 0.421233 0.221041 0.123445 0.300129
julia> # group results by testing set labels for color coding
setosa = Yte[:,Xte_labels.=="setosa"]
3×25 Array{Float64,2}:
2.72714 2.75491 2.32396 2.65105 2.68917 …
-0.230916 -0.406149 0.646374 0.0828144 -0.17411
0.253119 0.0271266 -0.230469 0.0252853 0.231507
julia> versicolor = Yte[:,Xte_labels.=="versicolor"]
3×25 Array{Float64,2}:
-0.901049 -0.189593 -0.631938 0.737306 0.00578031 …
0.350685 -0.7887 -0.40525 -1.01982 -0.74682
-0.0027406 0.291058 0.0207768 0.121331 -0.179235
julia> virginica = Yte[:,Xte_labels.=="virginica"]
3×25 Array{Float64,2}:
-1.4126 -1.95359 -3.35517 -2.89581 -2.8711 …
-0.556727 -0.133821 0.692925 0.487134 0.828406
-0.214115 -0.075898 0.293002 0.386084 -0.496979
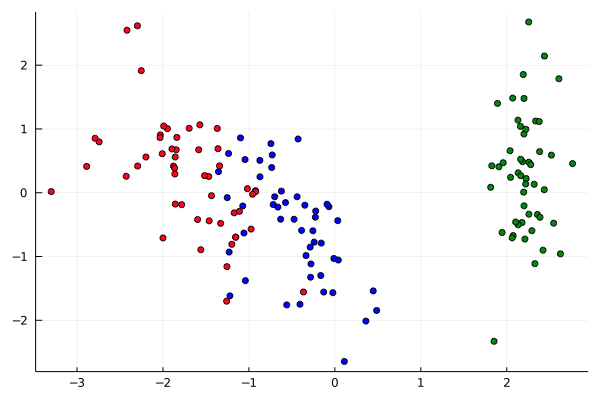
julia> # visualize first 3 principal components in 3D interacive plot
p = scatter(setosa[1,:],setosa[2,:],setosa[3,:],marker=:circle,linewidth=0)
julia> scatter!(versicolor[1,:],versicolor[2,:],versicolor[3,:],marker=:circle,linewidth=0)
julia> scatter!(virginica[1,:],virginica[2,:],virginica[3,:],marker=:circle,linewidth=0)
julia> plot!(p,xlabel="PC1",ylabel="PC2",zlabel="PC3")

その他,fit(PCA,...) が返すオブジェクトの出力
julia> indim(M) # 入力データ行列の次元数(変数の個数)
4
julia> outdim(M) # 結果の次元数(抽出された主成分の数)
3
julia> using Statistics
julia> mean(M) # 入力データの各変数の平均値
4-element Array{Float64,1}:
5.839999999999999
3.0640000000000005
3.775999999999999
1.2186666666666668
julia> projection(M) # 固有ベクトル(列が各主成分)
4×3 Array{Float64,2}:
-0.3419 0.740952 0.505693
0.109668 0.641943 -0.680395
-0.857598 -0.171424 -0.0624452
-0.368242 -0.0975392 -0.526723
julia> principalvars(M) # 固有値(求めた主成分の数だけ)
3-element Array{Float64,1}:
4.306799211542801
0.21643663210761893
0.10023939904836703
julia> tprincipalvar(M) # 固有値の和(求めた主成分の数まで)
4.623475242698786
julia> tresidualvar(M) # 固有値全体の和からtprincipalvar(M) を引いたもの
0.019814847391297796
julia> tvar(M) # 固有値全体の和
4.643290090090084
全ての固有値は,4.30679921, 0.21643663, 0.10023940, 0.01981485
julia> principalratio(M) # 寄与率 tprincipalvar(M) / tvar(M)
0.9957325846529409
R では prcomp() で行う。
R> data = t($Xtr)
R> colMeans(data)
[1] 5.840000 3.064000 3.776000 1.218667
Julia では,データの中心化(平均値を0にする)はするが尺度調整(標準偏差を1にしない)はしないのでそれに合わせる(R でもデフォルトは Julia と同じ)
R> ans = prcomp(data, center = TRUE, scale. = FALSE)
R> ans$rotation # 固有ベクトル
PC1 PC2 PC3 PC4
[1,] 0.3419004 -0.7409515 0.50569328 -0.2799450
[2,] -0.1096682 -0.6419429 -0.68039532 0.3360720
[3,] 0.8575983 0.1714240 -0.06244523 0.4808737
[4,] 0.3682420 0.0975392 -0.52672299 -0.7598992
R> ans$sdev^2 # 固有値
[1] 4.30679921 0.21643663 0.10023940 0.01981485
R> sum(ans$sdev^2) # tvar(M)
[1] 4.64329
R> sum(ans$sdev[1:3]^2) # tprincipalvar(M)
[1] 4.623475
R> test = t($Xte) # テストデータ
R> test2 = t(t(test) - colMeans(data)) # 平均値を 0 にする
R> score = test2 %*% ans$rotation[,1:3] # 主成分得点を計算
R> library(rgl) # 3次元散布図
R> plot3d(score$x[,1], score$x[,2], score$x[,3], col=rep(c("red", "black", "green"),each=25))